Ученые ФИЦ ИЦиГ СО РАН и НГУ выявили два фрагмента некодирующей ДНК, ответственных за реакцию на появление гормона ауксина в клетках и тканях. Коллеги российских исследователей из Голландии и Испании экспериментально подтвердили, что эти участки ДНК действительно играют важную роль в регуляции ответа на главный растительный гормон. Например, блокирование лишь одного из фрагментов приводит к ослаблению растения. Также зарубежным ученым удалось обосновать и прогноз новосибирцев о том, что одна из найденных последовательностей отвечает не только за активацию работы ауксин-чувствительных генов, но и, в некоторых случаях, за подавление. Результаты совместной работы опубликованы в PNAS.
Гормон ауксин управляет протеканием практически всех процессов у растения с помощью специальных белков ответа на ауксин. Однако до сих пор неизвестны подробности того, по какому принципу белки «выбирают» те или иные гены, чтобы запустить их работу. Международной группе ученых удалось закрыть часть белых пятен благодаря инициативе новосибирских биоинформатиков, которые специализируются на анализе полногеномных, а именно — транскриптомных данных. Последние дают сведения о том, какие гены активны в клетках или тканях.
«Мы начали этот проект давно, более семи лет назад. Мне было интересно понять, как ауксин — очень простое химическое соединение, регулирует почти каждое “движение” растения. Сделав распознавание данных, находящихся в открытом доступе, мы буквально “на кончике пера” открыли один из механизмов регуляции, обнаружив два элемента, которые очень часто встречаются в ауксин-чувствительных генах. Наши зарубежные коллеги подтвердили, что найденные последовательности играют значимую роль в регуляции ответа на гормон. Экспериментаторы генно-инженерным способом вводили мутации в ДНК, получали трансгенные растения, и выяснили, что если у них “выключить” даже одну из последовательностей, то меняется облик растения. В частности, у корня остается один сосудистый пучок вместо двух — организм ослабевает», — говорит старший научный сотрудник лаборатории компьютерной транскриптомики и эволюционной биоинформатики ФЕН НГУ, ведущий научный сотрудник ФИЦ ИЦиГ СО РАН кандидат биологических наук Виктория Владимировна Миронова, руководившая работой новосибирской научной группы.
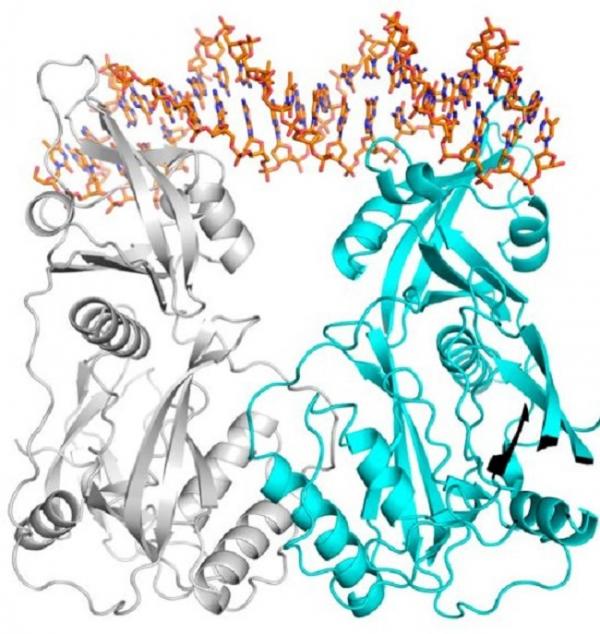
Обнаруженные последовательности отвечают за присоединение специальных белков, реагирующих на гормон и запускающих транскрипцию — считывание генетической информации. Ученые ФИЦ ИЦиГ СО РАН и НГУ предсказали, что одна из последовательностей, состоящая из нуклеотидов TGTCGG гораздо более «привлекательна» для белков раннего ауксинового ответа, чем известная ранее и считавшаяся канонической последовательность TGTCTC.
Специалисты университета Вагенингена (Голландия) и Центра синхротронного излучения Альба (Испания) реконструировали кристаллографическую структуру ДНК. В результате исследователи увидели, что белки ауксинового ответа образуют дополнительную водородную связь с последовательностью TGTCGG и поэтому «предпочитают» взаимодействовать именно с этим фрагментом ДНК.
«Детализировав кристаллическую структуру с использованием синхротронного излучения, наши коллеги физически обосновали то, что мы обнаружили биоинформатическими методами», — подчеркивает Виктория Миронова.
Весной 2020 года новосибирские исследователи обработали массивы данных RNA-seq. Это наиболее современный метод изучения экспрессии генов. На предыдущих этапах работа велась с датасетами, произведёнными менее точным и чувствительным методом микрочипирования. Новые сведения позволили, во-первых, подтвердить правильность первоначальных выводов, а во-вторых, обнаружить связь одной из последовательностей не только с увеличением экспрессии гена в ответ на ауксин, а еще и со слабым ее подавлением.
«Моя задача состояла в сборе и обработке преимущественно RNA-seq данных, полученных при обработке растений ауксином. Причем нужно было выбрать те, для которых время обработки было от одного до шести часов, так как нам требовалось проверить регуляцию раннего ответа на гормон. Мне предстояло определить парные последовательности, наиболее часто встречающиеся в промоторах — областях генов, которые отвечают за старт считывания генетической информации. Такие участки ДНК действительно обнаружились, и у одного из них мы нашли связь не только с активацией транскрипции, но и с ее подавлением», — объясняет соавтор статьи, аспирантка ФИЦ ИЦиГ СО РАН Яна Геннадьевна Сизенцова.
Яна Сизенцова, выпускница факультета естественных наук НГУ 2017 года проводит анализ данных, используя язык программирования R: сначала обрабатывает «сырые» данные — выравнивает их, затем сравнивает средние значения, выявляет статистически значимые, проводит коррекцию на множественное тестирование, объединяя несколько наборов данных. Последнее помогает избежать так называемой ошибки первого рода, когда различия между средними значениями ошибочно считаются значимыми.
«Я очень хотела заниматься биофинформатикой, поэтому в 2018 году пришла в группу Виктории Мироновой. Ранее я работала в лаборатории иммуногенетики Института молекулярной и клеточной биологии СО РАН, одно из научных направлений подразделения — разработка готовых противоопухолевых агентов, в частности CAR-T клеток. Тематики предыдущей и текущей моей научной деятельности, конечно, сильно отличаются, но я считаю, что человек должен быть готов осваивать любые методы. Кроме того, когда исследователь владеет биоинформатическими технологиями, методами статистики, то он может провести систематический, прицельный поиск ключевого объекта. Это на порядки более результативное прогнозирование, чем, если использовать, например, лишь литературные данные», — добавляет Яна Сизенцова.
По мнению Виктории Мироновой, найденные закономерности можно в перспективе применять для управления приспособляемостью растения к внешним факторам. Причем, не привнося в растение чужеродных фрагментов ДНК, а лишь блокируя какие-либо участки в некодирующей части ДНК, которая еще совсем недавно считалась «мусорной». Такая методика принципиально отличается от разработки трансгенных растений, когда в ДНК вводится ген растения другого вида.
Исследования выполнялись при поддержке Российского фонда фундаментальных исследований: гранты №18-04-01130 и №18-29-13040, бюджетного проекта № 0324-2019-0040-C-01.
Лаборатория компьютерной транскриптомики и эволюционной бифоинформатики ФЕН НГУ,
Сектор системной биологии морфогенеза растений ФИЦ ИЦиГ СО РАН
- Войдите или зарегистрируйтесь, чтобы отправлять комментарии